CRISPR好不好用,还要看基因?张锋成果获PNAS报道验证!
| 导读 | 刊登在PNAS上面自美国和加拿大研究人员的研究结果显示:个体基因编码的差异性可能会对基于应用CRISPR/Cas9基因编辑技术治疗方案的有效性、副作用及安全性产生影响。而这也验证了今年7月份张锋在《Nature》子刊上面发表的论文结果。 |
来自哈佛医学院、波士顿儿童医院和蒙特利尔大学的研究团队发现“一刀切”的基因编辑疗法可能并不会对所有患者产生有相同的疗效,基因编辑技术或许也需要根据每位患者的基因序列加以调整,以实现最大化的功效和防止潜在有害的脱靶效应。
“人类的基因序列各有不同,而将“标准化”的基因序列作为参考并不能顾及所有差异性,”来自达纳法伯波士顿儿童癌症和血液疾病中心的医学博士Stuart Orkin说。“我们建议将基因序列常见的变异纳入治疗性基因编辑的设计靶向系统中,以实现治疗疗效的最大化和潜在危险的最小化”。
研究人员在“美国科学院学报”(PNAS)的一篇题为“Human genetic variation alters CRISPR-Cas9 on- and off-targeting specificity at therapeutically implicated loci”的论文中报告了他们的发现。

目前在临床上已经开始进行CRISPR/Cas9基因编辑有效性的评估。“我们不仅需要评估是否可以成功的有效性,还应该考虑一旦脱靶带来的后果。”作者指出。“这需要评估与试剂递送、基因编辑试剂本身和脱靶有关的毒性”。
为了帮助理解基因编辑技术靶向和脱靶的潜在效应和帮助设计有效且安全的引导RNA(gRNA),大多数研究都是基于参考基因组或者细胞系基因组。
作为一种替代疗法,哈佛医学院的Matthew Canver教授领导了一次评估个体间遗传变异对CRISPR/Cas9基因编辑潜在性影响的研究,他们分析了7444个之前公布的人类全基因组序列和一个包含了大约300个不同的gRNA列表,这份列表上的gRNA可用于在基因组上30个不同的治疗相关位点的靶向定位。
他们的的结果表明,大约一半的gRNAs可以被小的基因变异、单核酸多态性或者包括gRNA自身在内的靶向位点的插入/删除所影响。
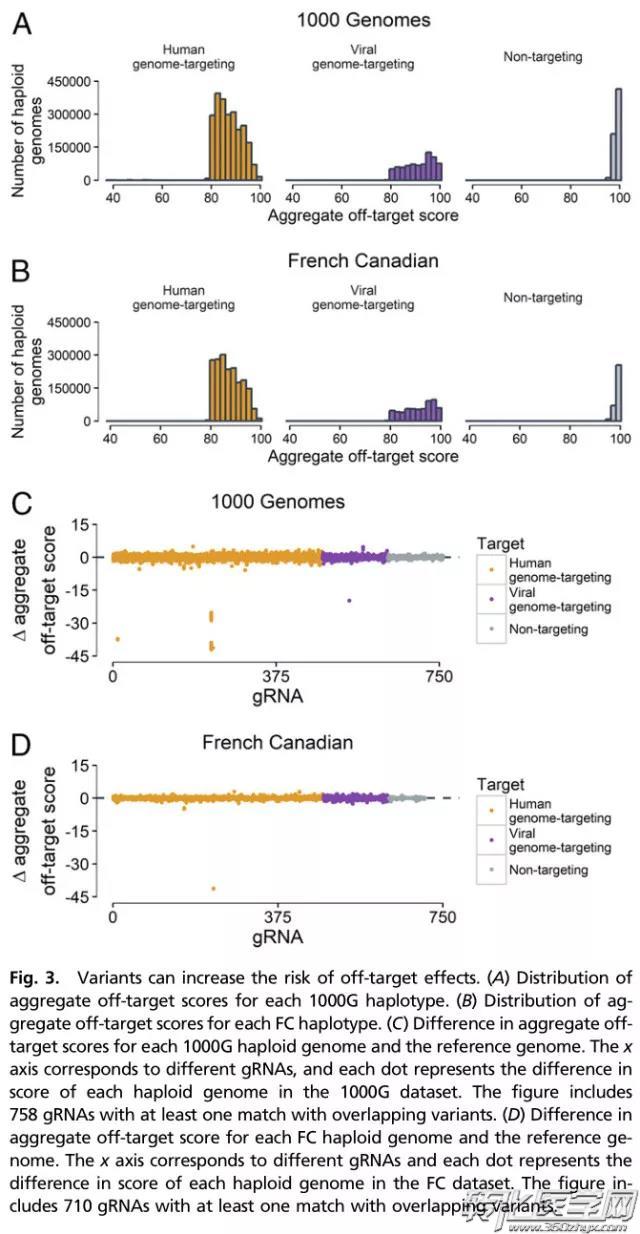
“如果CRISPR试剂的靶向治疗位点存在基因差异性,这将会有降低治疗疗效或者治疗失败的风险。”Carnver解释道。“由于与gRNA不匹配,一个碱基对所产生的基因差异性可能会导致结合效率下降。总的来说,这可能会导致治疗疗效的降低”。
研究显示,在一些情况下,基因变异甚至可能引导gRNA将CRISPR试剂导向基因组上的错误位点。“在一些罕见案例中,可能产生非常有效的“脱靶”位点——CRISPR试剂可能会在这些位点无意地剪切和结合。如果脱靶效应恰好发生在一个肿瘤抑制基因,这将是一个大问题”。
虽然这项研究专注于CRISPR/Cas9基因编辑,但研究小组表示研究结果可能对其他基因编辑技术(如锌指核酸酶和转录激活物样(TAL)效应核酸酶(TALENs))的设计有所影响。
“一致的观点认为所有这些技术均依赖于十分特异性地识别DNA碱基段,”Carnver说。“因此,影响靶向序列的变异体可能会降低gRNA的结合。变异体也可能会导致在可能造成伤害的新位点上的结合。随着基因编辑治疗持续发展并开始引入临床,确保每个治疗方案都是为即将治疗患者量身定做的,这一点意义重大”。
在他们的文章中,研究人员主张进行临床前研究以确保在gRNA设计阶段就考虑到基因变异并为临床翻译验证这些gRNA。
总目标是尽可能地为不同基因型患者提供“安全、有效、个性化”的治疗方案。他们进一步指出,在每位患者治疗前进行全基因组测序(WGS)不失为一种慎重的做法。“WGS数据允许他们在计算机上进行靶向和脱靶分析,这可以在患者接受治疗之前明确可能出现的治疗失败或不良结果。排除在抑癌基因等重要基因内或临近的可预测脱靶位点上的gRNA,这或许是为安全性考虑的明智之举”。
而在今年7月份的时候,CRISPR/Cas9基因编辑张锋已经在《Nature》子刊上面刊登了一篇自己的报道,表明在使用CRISPR/Cas9基因编辑系统的时候,个体化的差异会导致基因编辑系统失效或者造成损害的情况出现,而如今,这一结果得到了数据的支持。

参考资料:Genetic Differences Could Impact Efficacy and Safety of CRISPR
(转化医学网360zhyx.com)
 腾讯登录
腾讯登录







还没有人评论,赶快抢个沙发